【应用简介】
SNP 检测主要针对基因组上单核苷酸位点变异进行分型分析,广泛应用于疾病易感风险评估、肿瘤分子分型、药物基因组学、遗传多态性分析、物种亲缘鉴定等领域。可精准解析基因位点差异,为疾病筛查、个体化用药指导及基础遗传学研究提供分子依据。
【技术原理】
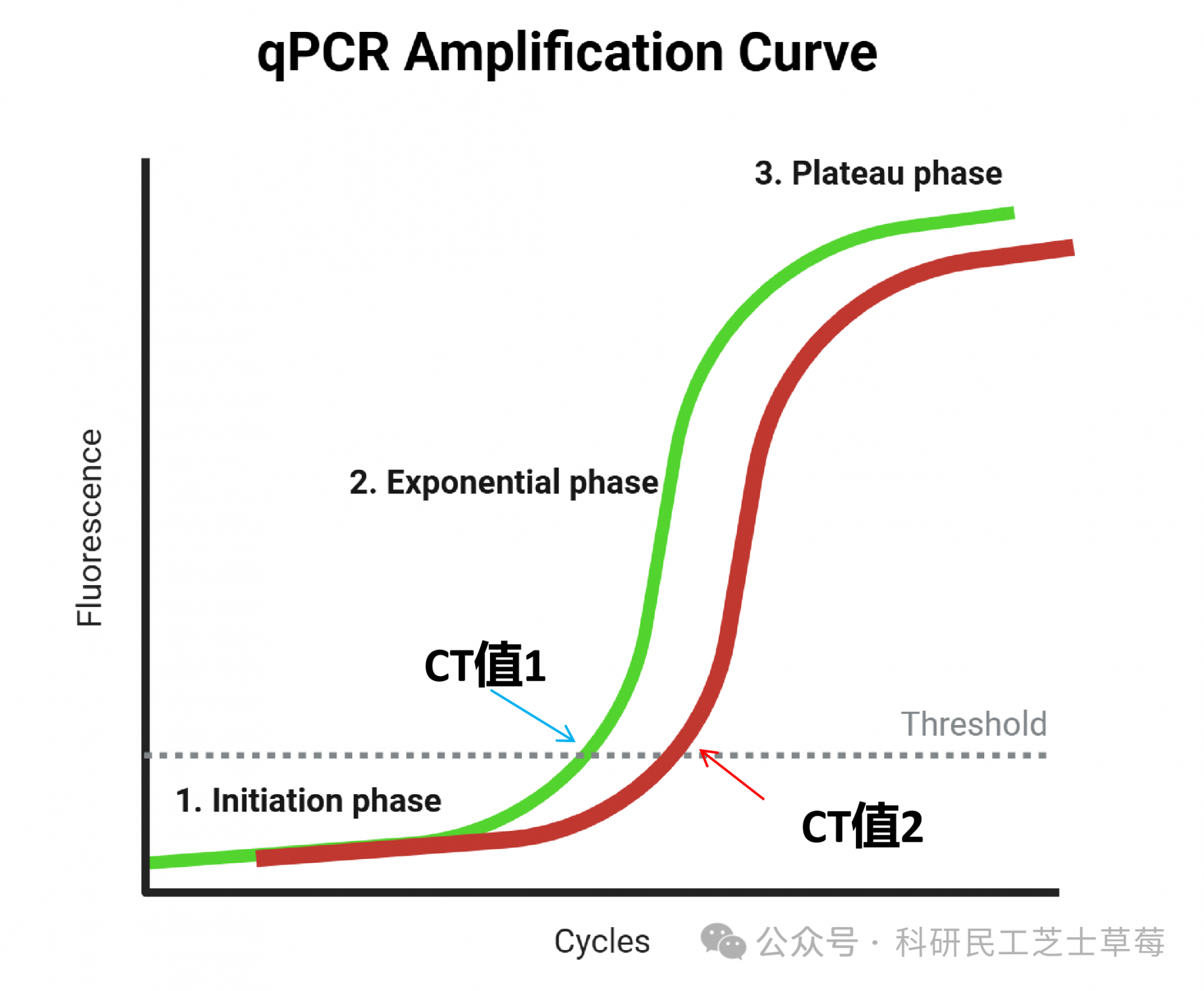
taqman探针法:针对染色体上的不同SNP位点分别设计PCR引物和TaqMan探针,进行实时荧光PCR扩增。探针的5’-端和3’-端分别标记一个报告荧光基团和一个淬灭荧光基团。当溶液中存在PCR产物时,该探针与模板退火,即产生了适合于核酸外切酶活性的底物,从而将探针5’-端连接的荧光分子从探针上切割下来,破坏两荧光分子间的PRET,发出荧光。通常用于少量SNP位点分析。
高分辨率熔解曲线分析(HRM)是近几年兴起的SNP研究工具,它通过实时监测升温过程中双链DNA荧光染料与PCR扩增产物的结合情况,来判断是否存在SNP,而且不同SNP位点、是否是杂合子等都会影响熔解曲线的峰形,因此HRM分析能够有效区分不同SNP位点与不同基因型。这种检测方法不受突变碱基位点与类型的局限,无需序列特异性探针,在PCR结束后直接运行高分辨率熔解,即可完成对样品基因型的分析。该方法无需设计探针,操作简便、快速,成本低,结果准确,并且实现了真正的闭管操作。

图:某基因的SNP(G>A)进行HRM分析的结果。左图为熔解曲线,右图为差异图
SNaPshot法:是基于荧光标记单碱基延伸原理的分型技术,也称小测序,主要针对中等通量的SNP分型项目。在一个含有测序酶、四种荧光标记ddNTP、紧临多态位点5’-端的不同长度延伸引物和PCR产物模板的反应体系中,引物延伸一个碱基即终止,经ABI测序仪检测后,根据峰的移动位置确定该延伸产物对应的SNP位点,根据峰的颜色可得知掺入的碱基种类,从而确定该样本的基因型。对于PCR产物模板可通过多重PCR反应体系来获得。通常用于10-30个SNP位点分析。
直接测序法:在所有SNP的检测方法中,对待检测片段进行直接扩增、测序是最为准确的方法,也是SNP分析的金标准。纯合型SNP位点的测序峰为单一峰型,而杂合型SNP位点的测序峰为套峰,因而很容易将其区分开来。通过直接测序方法进行SNP检测的检出率接近100%。该技术主要通过直接测序的方法来确定位点的基因型,这种分型方法准确性最高,但费用大。如果需要检测的几个SNP位点正好位于一个测序单元内(长度小于700 bp),则单个位点的分型费用可显著降低,这种分型技术不失为一种良好选择。对于准确性要求特别高或样本量特别小(几个或几十个)的项目,这种分型技术很适合。
【实验方法】
1、变性阶段
高温条件下,双链模板 DNA 发生热变性解链,解离为单链 DNA 模板;体系内上游 / 下游引物、两端分别标记荧光发光基团(Fluorophore,F)与荧光淬灭基团(Quencher,Q)的特异性 TaqMan 探针均处于游离单链状态。
2、退火结合阶段
体系温度降低,引物与单链模板 DNA 的互补序列特异性结合;同时TaqMan 特异性探针精准杂交结合至模板 DNA 引物之间的目的靶序列区域。
此时 DNA 聚合酶(Taq 酶)结合至引物结合位点,沿模板链启动 DNA 链延伸过程;探针依旧保持完整结构,荧光淬灭效应仍存在,体系依旧无有效荧光信号释放。
3、延伸酶切阶段
DNA 聚合酶沿模板链进行 5’→3’方向链延伸合成;当聚合酶行进至探针结合位置时,依靠自身5’→3'核酸外切酶活性,将结合在模板上的探针从 5’端开始逐步酶切降解。探针被切割后,荧光发光基团(F)与淬灭基团(Q)发生空间分离,二者间的荧光共振能量转移(FRET)效应消失,发光基团的荧光抑制解除,释放可被仪器检测的特异性荧光信号。DNA 链持续延伸,探针不断被酶切降解,随着循环数增加,荧光信号持续累积增强。
【送检标准】

【交付标准】
1、实验报告
2、真实实验结果
3、原始图片
4、实验原始数据
5、剩余物料在周期内可返还(超过周期,不予返还)